|
|
|
|
|
QB期刊 | 基于疾病子图位置编码的图Transformer用于改进共病预测 |
|
|
论文标题:Graph transformer with disease subgraph positional encoding for improved comorbidity prediction
期刊:Quantitative Biology
作者:Xihan Qin, Li Liao
发表时间:28 Aug 2025
DOI:10.1002/qub2.70008
微信链接:点击此处阅读微信文章
共病(多种疾病同时发生)预测是精准医疗的关键环节,但现有基于人类蛋白质相互作用组(HI)的方法面临难以逾越的技术瓶颈,如位置编码局限:传统方法(如拉普拉斯位置编码 LPE)仅捕捉聚类信息,忽略疾病亚图的标签关联,无法完整表征节点的疾病属性;特征捕捉不足:未能有效融合蛋白质节点连接性与疾病亚图关联,难以挖掘共病背后的分子机制;预测性能有限:面对不平衡的临床数据集,现有模型的区分能力不足,ROC AUC 与准确率有待提升;泛化能力薄弱:对不同共病定义阈值(如 RR0、RR1)的适配性差,难以满足多样化临床场景需求。这些痛点导致共病预测结果不够精准,无法为临床决策提供可靠支撑,成为疾病管理的 “拦路虎”。
近期,Quantitative Biology 发表了一篇来自美国特拉华大学Xihan Qin和Li Liao团队的研究性论文“Graph transformer with disease subgraph positionalencoding for improved comorbidity prediction ”,提出含疾病亚图位置编码的图 Transformer 模型(TSPE),通过整合聚类信息与疾病关联特征,解决传统共病预测中位置编码不足的核心问题,在临床基准数据集上实现性能大幅突破,为疾病管理与治疗方案优化提供精准工具。

全文概要
针对传统模型编码信息不全、特征融合不足、预测精度有限的三大瓶颈,团队构建了 TSPE 创新框架——以 Transformer 注意力机制捕捉蛋白质节点交互,提出亚图位置编码(SPE) 整合拉普拉斯位置编码(LPE)的聚类信息与图编码器嵌入位置编码(GPE)的疾病关联信息,通过 Node2Vec 生成节点嵌入,结合无掩码多头注意力实现共病二元分类。经实证,该模型在 RR0 和 RR1 基准数据集上表现突出:RR0 数据集 ROC AUC 达 0.9489,较现有最优方法(BSE_SVM)提升 28.24%,准确率提升 3.04%;RR1 数据集 ROC AUC 达 0.8009,提升 15.40%,准确率提升 4.93%。消融实验证实,SPE 显著优于 LPE 和无编码(NoPE),Matthews 相关系数(MCC)提升 2.38% 以上。该模型为共病预测提供了更全面的特征表征方案,未来将拓展至更大规模 HI 数据集,优化泛化能力并探索多疾病交互预测场景。
核心架构与流程
TSPE 采用 “节点嵌入—亚图编码—Transformer 编码 —分类输出” 的四步流程(图1):
1.节点嵌入生成:通过 Node2Vec 对 HI 中的蛋白质节点进行嵌入,捕捉网络结构特征;
2.SPE 编码整合:将 LPE(聚类信息)与 GPE(疾病亚图标签信息)融合,生成最终位置编码,公式如下:E=[(M+LPE),GPE]其中M为节点嵌入矩阵,通过奇异值分解(SVD)降低 GPE 维度,确保编码维度一致性;
3.Transformer 编码:编码器与解码器均采用无掩码多头注意力机制,捕捉疾病亚图间的节点交互;
4.分类输出:通过列 - wise L2 范数加权求和与 sigmoid 激活函数,实现共病二元分类,损失函数采用二元交叉熵(BCE)。
图示呈现从疾病 A、B 的相关蛋白质节点,经 Node2Vec 嵌入、SPE 编码,到 Transformer 编码器 - 解码器处理,最终输出共病预测结果的完整流程,核心是 SPE 编码与注意力机制的结合
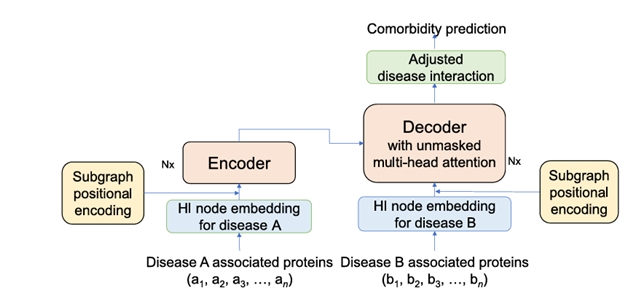
图1. TSPE 模型架构示意图
关键编码方法对比
团队创新提出的 SPE,解决传统编码信息不全的问题,三类编码方法差异如下(图2):
•LPE(拉普拉斯位置编码):仅捕捉图聚类信息,无法识别节点的疾病亚图归属;
•GPE(图编码器嵌入位置编码):基于已知亚图信息生成权重矩阵,突出疾病关联,但缺乏全局聚类特征;
•SPE(亚图位置编码):通过拼接(M+LPE)与 GPE,同时整合聚类信息与疾病标签关联,实现更全面的节点表征。
左图为 LPE 仅覆盖连通组件内节点,中图为 GPE 突出疾病亚图关联,右图为 SPE 融合两者优势,同时捕捉聚类与疾病归属信息
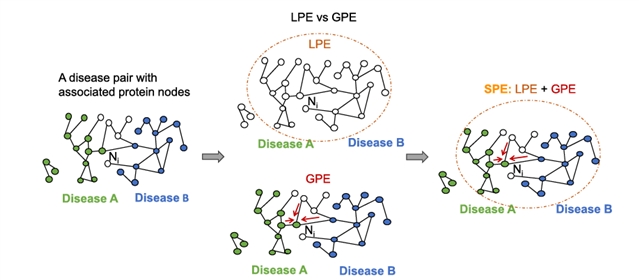
图 2. 不同位置编码方法对节点 N?的表征对比
核心数学方程
拉普拉斯矩阵与归一化:
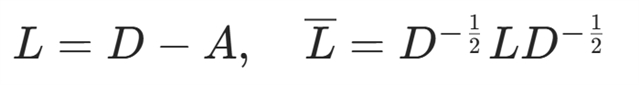
其中D为度矩阵,A为邻接矩阵,用于 LPE 的特征分解;
GPE 生成(基于 SVD 降维):
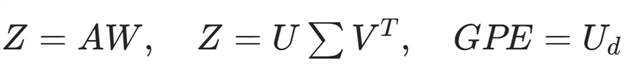
其中W为疾病亚图权重矩阵,Ud为前 d个左奇异向量;
分类输出加权:
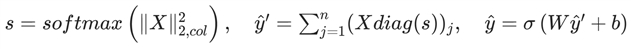
实证效果
团队在 RR0(RR>0 为共病)和 RR1(RR≥1 为共病)两个临床基准数据集上进行 10 折交叉验证,结果显著优于现有方法。
总结
本研究创新性地将亚图位置编码(SPE)与 Transformer 注意力机制结合,构建 TSPE 模型,突破传统共病预测中位置编码的局限。通过整合人类蛋白质相互作用组的结构特征与疾病亚图的关联信息,TSPE 在临床数据集上实现性能大幅提升,为共病预测提供了更精准、全面的技术方案,彰显了图深度学习在生物医学领域的应用潜力。
QB期刊介绍
Quantitative Biology (QB)期刊是由清华大学、北京大学、高教出版社联合创办的全英文学术期刊。QB主要刊登生物信息学、计算生物学、系统生物学、理论生物学和合成生物学的最新研究成果和前沿进展,并为生命科学与计算机、数学、物理等交叉研究领域打造一个学术水平高、可读性强、具有全球影响力的交叉学科期刊品牌。
《前沿》系列英文学术期刊
由教育部主管、高等教育出版社主办的《前沿》(Frontiers)系列英文学术期刊,于2006年正式创刊,以网络版和印刷版向全球发行。系列期刊包括基础科学、生命科学、工程技术和人文社会科学四个主题,是我国覆盖学科最广泛的英文学术期刊群,其中12种被SCI收录,其他也被A&HCI、Ei、MEDLINE或相应学科国际权威检索系统收录,具有一定的国际学术影响力。系列期刊采用在线优先出版方式,保证文章以最快速度发表。
中国学术前沿期刊网
http://journal.hep.com.cn

特别声明:本文转载仅仅是出于传播信息的需要,并不意味着代表本网站观点或证实其内容的真实性;如其他媒体、网站或个人从本网站转载使用,须保留本网站注明的“来源”,并自负版权等法律责任;作者如果不希望被转载或者联系转载稿费等事宜,请与我们接洽。