|
|
|
|
|
小核糖核酸病毒复制新机制:3C/3CD蛋白与病毒RNA的多价相互作用驱动液-液相分离 | MDPI Viruses |
|
|
论文标题:Multivalent Interactions Between the Picornavirus 3C(D) Main Protease and RNA Oligonucleotides Induce Liquid–Liquid Phase Separation
论文链接:https://www.mdpi.com/1999-4915/17/11/1473
期刊名:Viruses
期刊主页:https://www.mdpi.com/journal/viruses
一、研究背景
3C蛋白酶(3C protease)及其前体3CD蛋白是小核糖核酸病毒(Picornavirus,如脊髓灰质炎病毒Poliovirus,PV、柯萨奇病毒Coxsackievirus)生命周期中不可或缺的多功能蛋白。它们不仅发挥蛋白酶活性,负责切割病毒多聚蛋白与宿主蛋白,还能通过3C结构域与病毒RNA基因组中的顺式作用复制元件(cis-acting replication elements,CREs)结合,调控病毒复制与翻译进程。然而,这些蛋白与RNA相互作用的分子机制及其潜在功能尚未明确。近日,美国宾夕法尼亚州立大学与德国马克斯·普朗克生物物理研究所的联合研究团队在Viruses期刊发表研究,综合运用生物物理与计算机模拟技术,首次揭示小核糖核酸病毒3C/3CD蛋白可通过与RNA发生多价相互作用,驱动液-液相分离(Liquid-Liquid Phase Separation, LLPS),系统阐明了其物理化学机制,并提出其在调控病毒复制与宿主互作中的潜在功能,为开发靶向相分离过程的抗病毒策略提供了理论依据。
二、研究内容
本研究采用结构生物学、生物物理学与计算生物学相结合的多尺度技术体系,系统揭示了小核糖核酸病毒3C/3CD蛋白与病毒RNA互作并驱动LLPS的完整分子机制。LLPS可能为病毒复制复合体提供空间组装的高浓度微环境,同时介导病毒与宿主应激颗粒的相互作用,并在调控病毒蛋白功能协同中发挥关键作用。研究团队展开以下五个部分的具体研究:
1. 核磁共振明确双位点RNA结合界面
通过核磁共振技术,对比分析了脊髓灰质炎病毒3C蛋白(PV-3C)在游离状态以及与RNA-1结合状态下的谱图变化(图1A)。结果显示,RNA结合引起多个残基发生显著化学位移扰动(Chemical Shift Perturbation, CSP)(图1B),主要聚集在两个区域:Cluster-I(含E81-H89及N端螺旋)与Cluster-II(含催化残基H40、E71及相邻区域)。静电势图谱(图1D)显示两区域均为连续正电表面,为其与RNA的静电结合提供了结构基础。Cluster-II与催化中心(His40/Glu71)的邻接则提示RNA结合可能通过变构效应调节蛋白酶活性。
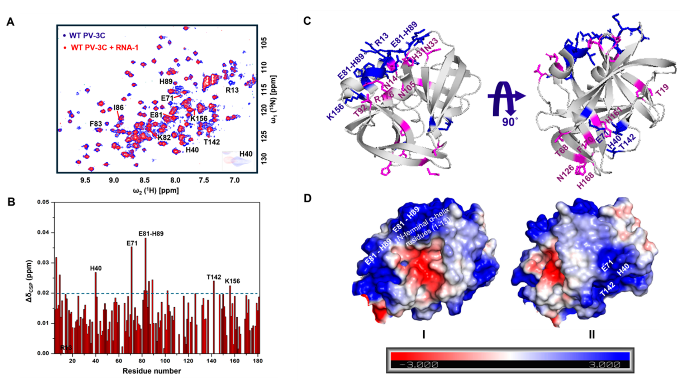
图1. RNA结合引起PV-3C蛋白两个反向残基簇的化学位移变化
2. 分析超速离心动态监测多价复合物的形成与组装过程
通过AUC分析型超速离心技术,检测3C蛋白与RNA-1在不同化学计量比下的组装状态(图2)。结果显示,在1:1比例下,体系主要形成单一复合物;当RNA比例提高至1:2及以上时,体系中逐渐出现沉降系数分布范围更宽的高分子量组分,表明形成了从二聚到多聚的连续组装体。该数据直观证实了蛋白与RNA之间存在化学计量依赖性的多价相互作用,即单个3C蛋白分子可同时结合多个RNA链,为后续LLPS的发生提供了分子聚集基础。
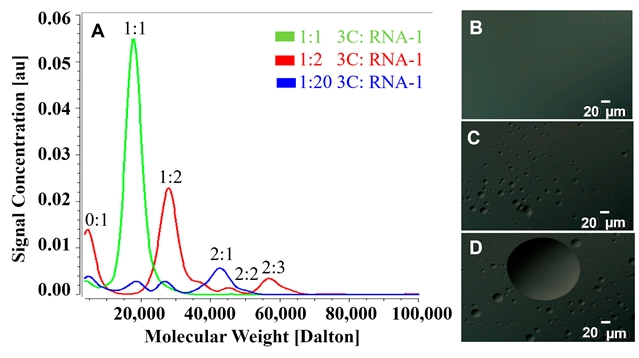
图2. PV-3C与RNA互作诱导多聚复合物形成与液-液相分离
3. 显微成像直接捕捉LLPS过程
基于多价相互作用的研究结果,研究团队进一步利用微分干涉差显微镜对3C/RNA-1体系进行了直接观测。显微图像显示(图2C-D),在RNA过量(≥1:2)的条件下,体系中出现大量动态的微米级液态凝聚体。这些凝聚体表现出典型的LLPS特征,包括液滴融合、分裂及布朗运动等物理行为。该现象在3CD蛋白与多种RNA的互作体系中也得到验证(图3),表明LLPS是3C结构域的固有特性。

图3. PV-3CD与RNA互作诱导液-液相分离
4. 分子动力学模拟揭示多价网络机制
基于分子动力学模拟(Molecular Dynamics, MD),研究团队从原子层面阐明了3C蛋白与RNA的多价相互作用机制(图4)。残基邻近概率(Proximity Probability, Pprox)分析显示(图4A),Cluster-I和Cluster-II区域均具有高RNA结合倾向,而距离分布图谱(图4B)则直观展示了RNA与这两个结合界面之间的稳定空间关联。模拟的构象快照(图4C)呈现了“蛋白-RNA-蛋白”交联网络结构。这些结果从原子尺度证实多价相互作用是驱动LLPS的关键物理机制。
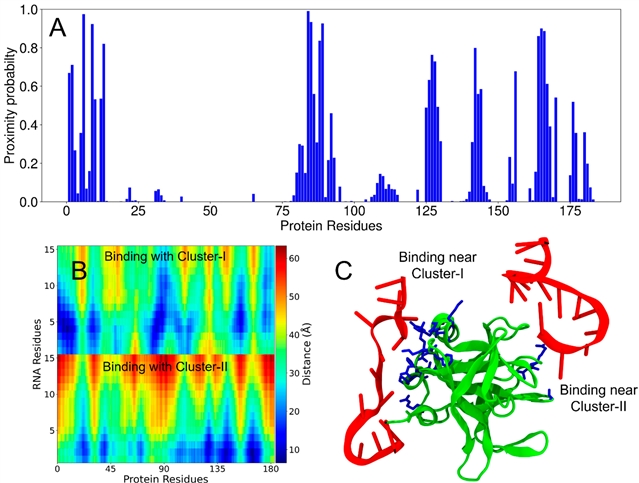
图4. 分子动力学模拟揭示PV-3C蛋白与RNA-1的两个相互作用位点
5. 功能构象模拟提示RNA结合调控蛋白功能
对全长3CD蛋白进行MD模拟(图5),残基邻近概率分析(图5A)与距离分布图谱(图5B)显示其Cluster-I和Cluster-II同样保持高RNA结合倾向。半径回转时序分析(Time Evolution of the Radius of Gyration, Rg)(图5E)表明,RNA结合能在约130纳秒内诱导3CD蛋白发生显著的构象压缩,导致3C与3D结构域间的空间距离缩短约15%。这一动态构象变化表明,RNA结合不仅通过多价相互作用促进相分离,还可能通过精准调控结构域间的空间排布,实现3C蛋白酶催化活性与3D聚合酶复制功能的高效协同,为理解病毒复制复合体(Viral Replication Complex, VRC)的动态组装机制提供了重要线索。
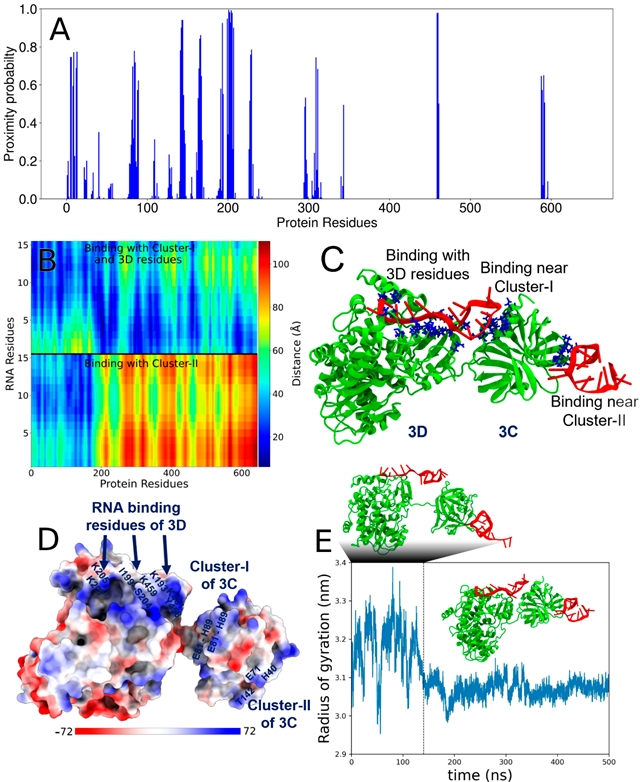
图5. 分子动力学模拟揭示PV-3CD蛋白与RNA-1的相互作用
三、研究发现与意义
本研究系统揭示了小核糖核酸病毒3C/3CD蛋白与病毒RNA通过多价相互作用驱动LLPS的新机制。研究发现,3C蛋白通过其两个正电荷界面(Cluster-I与Cluster-II)与RNA广泛结合,在RNA过量条件下形成多价网络并诱导LLPS。RNA结合还可诱导3CD蛋白构象压缩,提示其在病毒复制中具有协同调控潜力。该研究首次将3C/3CD蛋白的功能研究拓展至相分离调控领域,阐明病毒可通过LLPS形成高浓度复制微环境、干扰宿主应激颗粒功能,并可能通过结构域空间重排协调酶活功能。这些发现不仅深化了对小核糖核酸病毒复制机制的理解,也为开发靶向“病毒蛋白-宿主细胞相互作用”的抗病毒策略提供了重要依据,同时为探索其他RNA病毒的致病机制提供了研究启示。
四、作者介绍
本研究由美国宾夕法尼亚州立大学化学系与德国马克斯·普朗克生物物理研究所合作完成。通讯作者David D. Boehr教授长期致力于病毒蛋白的动力学与功能机制研究;第一作者Somnath Mondal博士专注于生物大分子磁共振以及相分离的计算机模拟技术。本研究获美国国立卫生研究院(NIH)项目支持。
Viruses 期刊介绍
主编:Eric O. Freed, Center for Cancer Research, National Cancer Institute, USA
涵盖人类病毒和病毒疾病,动物病毒,植物病毒,病毒免疫、疫苗和抗病毒药物以及朊病毒等各方面研究,目前已被SCIE (Web of Science)、MEDLINE (PubMed) 等数据库收录。
|
2024 Impact Factor
|
3.5
|
|
2024 CiteScore
|
7.7
|
|
Time to First Decision
|
17.2 Days
|
|
Acceptance to Publication
|
2.7 Days
|
特别声明:本文转载仅仅是出于传播信息的需要,并不意味着代表本网站观点或证实其内容的真实性;如其他媒体、网站或个人从本网站转载使用,须保留本网站注明的“来源”,并自负版权等法律责任;作者如果不希望被转载或者联系转载稿费等事宜,请与我们接洽。